Bacteria gramnegativa
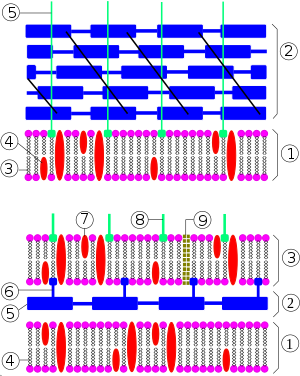
Abajo: Bacteria gramnegativa. 1-membrana citoplasmática (membrana interna), 2-espacio periplasmático, 3-membrana externa, 4-fosfolípidos, 5-peptidoglicano, 6-lipoproteína, 7-proteínas, 8-lipopolisacáridos, 9-porinas.
Las bacterias gramnegativas son bacterias que no se tiñen de azul oscuro o de violeta por la tinción de Gram, y lo hacen de un color rosado tenue: de ahí el nombre de "gramnegativas" o también "Gram-negativas".[1] Esta característica está íntimamente ligada a la estructura didérmica dada por la envoltura celular, porque presenta doble membrana celular (una externa y la otra citoplasmática), lo que refleja un tipo natural de organización bacteriana. Son uno de los principales supergrupos de bacterias, y cuando se tratan como taxón se utiliza también el nombre Negibacteria[2] o el de Didermata. Las restantes son las bacterias grampositivas.
Las bacterias gramnegativas presentan dos membranas lipídicas entre las que se localiza una fina pared celular de peptidoglicano, mientras que las bacterias grampositivas presentan solo una membrana lipídica y la pared de peptidoglicano es mucho más gruesa. Al ser la pared fina, las gramnegativas no retienen el colorante durante la tinción de Gram.[3]
Muchas especies de bacterias gramnegativas causan enfermedades. Algunos cocos gramnegativos causan la gonorrea (Neisseria gonorrhoeae), la meningitis (Neisseria meningitidis) y síntomas respiratorios (Moraxella catarrhalis), entre otros. Los bacilos gramnegativos incluyen un gran número de especies. Algunos de ellos causan principalmente enfermedades respiratorias (Haemophilus influenzae, Klebsiella pneumoniae, Legionella pneumophila, Pseudomonas aeruginosa), enfermedades urinarias (Escherichia coli, Proteus mirabilis, Enterobacter cloacae, Serratia marcescens) y enfermedades gastrointestinales (Helicobacter pylori, Salmonella enteritidis, Salmonella typhi). Otros están asociadas a infecciones nosocomiales (Acinetobacter baumanii).
Estructura
[editar]La envoltura celular de las bacterias gramnegativas está compuesta por una membrana citoplasmática (membrana interna), una pared celular delgada de peptidoglicano, que rodea a la anterior, y una membrana externa que recubre la pared celular de estas bacterias.[4] Entre la membrana citoplasmática interna y la membrana externa se localiza el espacio periplásmico, relleno de una sustancia denominada periplasma, la cual contiene enzimas importantes para la nutrición en estas bacterias.
La membrana externa contiene diversas proteínas; entre ellas, las porinas o canales proteicos que permiten el paso de ciertas sustancias. También presenta unas estructuras llamadas lipopolisacáridos (LPS), que están formados por tres regiones: el polisacárido O (antígeno), una estructura polisacárida central (KDO) y el lípido A (endotoxina). El lipopolisacárido contiene una toxina termoestable que se libera al romperse la bacteria gramnegativa, pudiendo resistir a la esterilización en autoclave.
Las bacterias gramnegativas pueden presentar una capa S que se apoya directamente sobre la membrana externa y no sobre la pared de peptidoglicano, como sucede en las gram positivas. Si presentan flagelos, estos tienen cuatro anillos de apoyo en lugar de los dos de las bacterias gram positivas (hay dos anillos por membrana). No presentan ácidos teicoicos ni ácidos lipoteicoicos, típicos de las bacterias grampositivas. Las lipoproteínas se unen al núcleo de polisacáridos, mientras que en las bacterias grampositivas estos no presentan lipoproteínas. La mayoría de las bacterias gramnegativas no forma endosporas (Coxiella burnetti, que produce estructuras similares a las endosporas, es una notable excepción).
Durante la tinción de Gram el colorante (cristal violeta) penetra en todas las células bacterianas (tanto grampositivas como gramnegativas) a través de la pared bacteriana. A continuación, la mezcla de alcohol-acetona decolora las bacterias gramnegativas (no así las grampositivas). Por último, un colorante de contraste (safranina o fucsina) vuelve a las bacterias gram negativas de color rosado, mientras que las grampositivas permanecen con color violeta-azul oscuro.
Patogenia y tratamiento
[editar]
Muchas especies de bacterias gramnegativas causan enfermedades. Una de las varias características únicas de las bacterias gramnegativas es la estructura de la membrana externa. La parte exterior de esta membrana comprende un complejo de lipopolisacáridos cuya parte lípida (el lípido A) actúa como una endotoxina y es responsable de la capacidad patógena del microorganismo.[1] Este componente desencadena una respuesta inmune innata que se caracteriza por la producción de citocinas y la activación del sistema inmunológico. La inflamación es una consecuencia común de la producción de citocinas, que también pueden producir toxicidad. Si la endotoxina entra en el sistema circulatorio, provoca una reacción tóxica con aumento de la temperatura y de la frecuencia respiratoria y bajada de la presión arterial. Esto puede dar lugar a un shock endotóxico, que puede ser fatal.
Esta membrana externa protege a las bacterias de varios antibióticos, colorantes y detergentes que normalmente dañarían la membrana interna o la pared celular de peptidoglicano. La membrana externa proporciona a estas bacterias resistencia a la lisozima y a la penicilina. Afortunadamente, se han desarrollado otros tratamientos alternativos para combatir la membrana externa de protección de estos patógenos, tales como la lisozima con EDTA y el antibiótico ampicilina. También pueden usarse otros fármacos, a saber, cloranfenicol, estreptomicina y ácido nalidíxico.
Filogenia de las bacterias gramnegativas
[editar]
Dentro del grupo de las bacterias gramnegativas es posible diferenciar dos niveles de organización, que se distinguen por la composición de la membrana externa.[5][6] En el primer subtipo la membrana externa presenta solo simples fosfolípidos, mientras que en el segundo subtipo además presenta la inserción de moléculas complejas de lipopolisacáridos (la estructura típica descrita anteriormente). Los primeros incluyen solamente a Thermotogae (termófilos y heterótrofos fermentativos) y a Deinococcus-Thermus (quimiorganotrofos extremófilos); estos últimos, aunque dan positivo en la tinción de Gram, son estructuralmente similares a las bacterias gramnegativas.
El resto de las bacterias gramnegativas pertenecen al segundo subtipo y presentan lipopolisacáridos en su membrana externa. Las proteobacterias son uno de los grupos principales, que incluyen a Escherichia coli, Salmonella y otras enterobacterias, Pseudomonas, Moraxella, Helicobacter, Stenotrophomonas, Bdellovibrio, bacterias del ácido acético, Legionella y las proteobacterias alfa, como Wolbachia, y muchas otras. Otros grupos notables son las cianobacterias, espiroquetas y las bacterias verdes del azufre y no del azufre.
Se desconoce si la doble membrana es una característica primitiva o derivada. Si fuese primitiva, las bacterias gramnegativas serían las primeras bacterias en originarse, con las grampositivas derivadas a partir de ellas.[7]
- Una opción es que las bacterias grampositivas fueran las que aparecieron primero, puesto que son las más simples. Se ha propuesto que cuando un grupo de estas bacterias desarrolló los mecanismos para producir antibióticos (como hace por ejemplo, la bacteria Streptomyces), la presión selectiva obligó a las demás a protegerse de los efectos de estas sustancias. Una de estas estrategias fue desarrollar una membrana externa, dando lugar a las bacterias gramnegativas.[8][6]
- La opción alternativa considera que la doble membrana es una característica primitiva y que la segunda membrana se perdió al crecer la pared de peptidoglicano que impide la transferencia de lípidos para formar la membrana externa.[9][2] La hipótesis del citoplasma fuera describe un posible modelo para la aparición de la doble membrana de las bacterias gramnegativas. Otro posible escenario para la aparición de la membrana externa es el de la esporulación.[7]
Véase también
[editar]- Bacteria grampositiva
- Bacterias gramnegativas con G-C bajo
- Envoltura celular bacteriana
- Monodérmico
- Tinción de Gram
Referencias
[editar]- ↑ a b Salton MJR, Kim KS (1996). Structure. in: Baron's Medical Microbiology (Baron S et al, eds.) (4th ed. edición). Univ of Texas Medical Branch. ISBN 0-9631172-1-1.
- ↑ a b Cavalier-Smith, T. (2006), Rooting the tree of life by transition analyses, Biol Direct. 1: 19. doi: 10.1186/1745-6150-1-19.
- ↑ Gram, HC (1884). «Über die isolierte Färbung der Schizomyceten in Schnitt- und Trockenpräparaten». Fortschr. Med. 2: 185-189.
- ↑ J. M. Ghuysen et al. (1994) Bacterial Cell Wall, Elsevier, ISBN 978-0-444-88094-9.
- ↑ Muñoz-Gómez, Sergio A., and Andrew J. Roger. Leaving negative ancestors behind. eLife 5 (2016): e20061.
- ↑ a b Gupta, Radhey S. Origin of diderm (Gram-negative) bacteria: antibiotic selection pressure rather than endosymbiosis likely led to the evolution of bacterial cells with two membranes. Antonie Van Leeuwenhoek 100.2 (2011): 171-182.
- ↑ a b Tocheva, Elitza I., Davi R. Ortega, and Grant J. Jensen. Sporulation, bacterial cell envelopes, and the origin of life. (2016).
- ↑ Gupta RS (2000). «The natural evolutionary relationships among prokaryotes». Crit. Rev. Microbiol. 26 (2): 111-131. PMID 10890353. doi:10.1080/10408410091154219.
- ↑ Cavalier-Smith, T. (2006). «Cell evolution and Earth history: stasis and revolution». Philos Trans R Soc Lond B Biol Sci 361 (1470): 969-1006. PMID 16754610. (enlace roto disponible en Internet Archive; véase el historial, la primera versión y la última).
