Haplogrupo P (ADNmt)
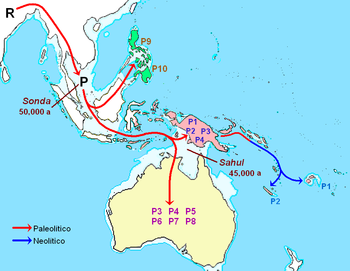
En genética humana el haplogrupo P es un haplogrupo mitocondrial típico de Sahul, tanto en aborígenes australianos como melanesios, con menor presencia en Insulindia. Desciende del macrohaplogrupo R, está definido por el marcador 15607 y se originó en el Sudeste de Asia hace unos 50.000 años.
Origen y dispersión[editar]
Múltiples autores coinciden en que este haplogrupo proviene de los pueblos del paleolítico de la región de la Sonda (Sudeste de Asia) con una antigüedad de 50.000 años,[1] dispersándose desde allí con los primeros colonizadores de Sahul (australianos, papúes) y Filipinas, por lo que probablemente es la marca genética más característica de los aborígenes de estas regiones y una huella de la antigua relación entre ellos.[2]
La dispersión del haplogrupo P a través de sus subclados, demostraría que los aborígenes de estas regiones tienen un origen común, en donde Sahul fue colonizada hace aproximadamente 46.000 años por una migración relativamente rápida de humanos modernos provenientes del Sudeste de Asia y sin ninguna evidencia de hibridación con poblaciones de Homo erectus; produciéndose un considerable aislamiento de los grupos nativos colonizadores y por largo tiempo (decenas de miles de años).[3]
Frecuencias[editar]
Australia: Se ha encontrado entre aborígenes australianos una frecuencia aproximada del 37.5%.
Melanesia: En Nueva Guinea promedios de 27%[1] y 41%,[4] siendo especialmente importante entre los papúes. En Papúa Nueva Guinea encontramos las frecuencias más altas en el archipiélago de las Luisiadas (al Sudeste) con 75% y en la zona montañosa occidental 61%,[1] descendiendo hacia las costas del Sur a 8%. Papúa Occidental presenta un 28%.
En las demás islas de Melanesia varía opteniendo 7% como promedio, encontrando las siguientes frecuencias:[4] En Nueva Caledonia 45%, Vanuatu 18%, Santa Cruz 9%, Fiyi 7%, Nueva Bretaña 4%, Bougainville 4%, Salomón 2-6% y Nueva Irlanda 2%.
Insulindia: Bajas frecuencias al este de Indonesia.[5] En Filipinas se ha encontrado recientemente en pequeñas frecuencias, promediando 1.4% y en sus variedades P9 (o P8) y P10.[2] En los negritos aeta de Bataan (Filipinas) se encontró 40%.[6]
Polinesia: Ausente o disperso en pequeñas frecuencias.
Distribución por subclados[editar]
Del haplogrupo P (15607) se derivan los siguientes clados:
- (16176)
- P1: Especialmente en Melanesia,[1] bien extendido y con las más altas frecuencias en las montañas de Nueva Guinea Oriental. En las Molucas 9% y menor frecuencia en la Polinesia (Tonga, Tuvalu) y en las islas menores de la Sonda.[7] Raro en Célebes y Sumba.[5]
- P2'10
- P2: En Melanesia,[1] especialmente en Nueva Guinea y Nueva Caledonia.
- P10: Al Sur de Filipinas.[2]
- P8 o P9 o AuE: En Australia,[8] región central
- P3: En Oceanía
- P3a: En Australia
- P3b: En Melanesia
- P4: En Oceanía
- P4a: En Melanesia[3]
- P4b o AuC: En Australia,[9] región de los ríos (parte centro-occidental de Nueva Gales del Sur)
- P5: En Australia
- P6: En Australia
- P7: En Australia
- P9 o P8: Norte de Filipinas
Véase también[editar]
- Haplogrupo MS (ADN-Y)
| Eva mitocondrial (L) | |||||||||||||||||||||||||||||||||||||||
| L0 | L1–6 | ||||||||||||||||||||||||||||||||||||||
| L1 | L2 | L3 | L4 | L5 | L6 | ||||||||||||||||||||||||||||||||||
| M | N | ||||||||||||||||||||||||||||||||||||||
| CZ | D | E | G | Q | A | I | O | R | S | W | X | Y | |||||||||||||||||||||||||||
| C | Z | B | F | R0 | R2'JT | P | U | ||||||||||||||||||||||||||||||||
| HV | JT | K | |||||||||||||||||||||||||||||||||||||
| H | V | J | T | ||||||||||||||||||||||||||||||||||||
Referencias[editar]
- ↑ a b c d e Jonathan Friedlaender et al 2005, Expanding Southwest Pacific mitochondrial haplogroups P and Q. Archivado el 19 de septiembre de 2009 en Wayback Machine. MBE Advance Access published April 6, 2005
- ↑ a b c Tabbada, Kristina. et al. 2009, Philippine mitochondrial DNA diversity: a populated viaduct between Taiwan and Indonesia? Archivado el 23 de noviembre de 2009 en Wayback Machine. Molecular Biology and Evolution, doi:10.1093/molbev/msp215
- ↑ a b Hudjashov, Georgi et al. 2007. Revealing the prehistoric settlement of Australia by Y chromosome and mtDNA analysis. PNAS May 22, 2007 vol. 104 no. 21 8726-8730
- ↑ a b D. Andrew Merriwether et al 2005, Ancient mitochondrial M haplogroups identified in the Southwest Pacific. PNAS September 13, 2005 102 37, 13034-13039
- ↑ a b Hill, Catherine et al 2006, A Mitochondrial Stratigraphy for Island Southeast Asia.
- ↑ Delfin F. et al 2013. Complete mtDNA genomes of Filipino ethnolinguistic groups: a melting pot of recent and ancient lineages in the Asia-Pacific region. Eur J Hum Genet. 2013 Jun 12. doi: 10.1038/ejhg.2013.122.
- ↑ Kayser, Manfred tl 2006, Melanesian and Asian Origins of Polynesians: mtDNA and Y Chromosome Gradients Across the Pacific
- ↑ Rosalind Harding 2006, Gene tree analyses of Aboriginal Australians. Archivado el 20 de septiembre de 2009 en Wayback Machine. University of Oxford
- ↑ van Holst Pellekaan 2006, Mitochondrial genomics identifies major haplogroups in Aboriginal Australians. Am J Phys Anthropol. 2006 Oct;131(2):282-94
Enlaces externos[editar]
- Haplogrupo P de Ian Logan
- Árbol filogenético de R de van Oven & Kayser 2009
