Proteína hierro-azufre
Las proteínas hierro-azufre son proteínas que se caracterizan por la presencia de centros hierro-azufre, que contienen varios grupos sulfuro unidos a entre dos y cuatro átomos de hierro en estados de oxidación variables. Se pueden encontrar centros hierro-azufre en diversas metaloproteínas, tales como ferredoxina, NADH deshidrogenasa, hidrogenasas, coenzima Q - citocromo c reductasa, succinato-coenzima Q reductasa y nitrogenasa.[1] Los centros hierro-azufre son más conocidos por su papel en las reacciones de oxidación-reducción como parte del transporte de electrones mitocondrial: tanto el complejo I como el complejo II tienen múltiples centros Fe-S. Poseen también otras funciones, como es el caso de la catálisis en la aconitasa, la generación de radicales en las enzimas dependientes de SAM, y como donantes de azufre en la biosíntesis del ácido lipoico y la biotina. Además, algunas proteínas Fe-S regulan la expresión génica. Las proteínas Fe-S son vulnerables al ataque del óxido nítrico biogénico.
Estructura[editar]
En casi todas las proteínas Fe-S la disposición de los átomos de Fe es tetraédrica y sus ligandos son azufres de grupos tiol de los residuos de cisteina. Cada grupo sulfuro establece dos o tres enlaces de coordinación con hierro. Son comunes tres tipos diferentes de centros Fe-S con estas características.
Centro 2Fe-2S[editar]

El centro [Fe2S2] es el sistema polimetálico más simple y está constituido por dos iones de hierro enlazados mediante dos iones de azufre y coordinados con cuatro ligandos de cisteína (Fe2S2 en ferredoxinas), o bien con dos cisteínas y dos histidinas (en las proteínas de Rieske). En la forma oxidada, las proteínas contienen dos iones Fe3+, mientras que en la reducida contienen un Fe3+ y un Fe2+. Los dos estados de oxidación corresponden a (FeIII)2 y FeIIIFeII.
Centro 4Fe-4S[editar]
Esta es una estructura común con cuatro iones de hierro y cuatro de azufre ubicados todos ellos en los vértices de un cubo. Los átomos de Fe están coordinados típicamente por ligandos de cisteína. Las proteínas transportadoras de electrones [Fe4S4] (como la ferredoxina) pueden a su vez subdividirse en ferredeoxinas de bajo potencial (de tipo bacteriano) y de alto potencial (HiPIP). Las ferredoxinas de bajo y alto potencial están relacionadas por el siguiente esquema redox:
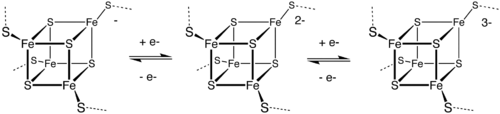
El centro HiPIP oscila entre Fe4S42+ y Fe4S43+ (respectivamente, [2Fe3+, 2Fe2+] y [3Fe3+, Fe2+]). Los potenciales de este par redox varían de 0,4 a 0,1 V. En las ferrodoxinas bacterianas, el par de estados de oxidación es Fe4S4+ y Fe4S42+ (correspondientes, respectivamente, a [Fe3+, 3Fe2+] y [2Fe3+, 2Fe2+]). Los potenciales para este par redox varían de -0.3 a -0.7 V. Las dos familias comparten el Fe4S42+. La diferencia en los pares redox se atribuye al número de puentes de hidrógeno que formen, que modifica fuertemente la basicidad de los ligandos tiolato de las cisteínas. Otro par redox aún más reductor que la ferrodoxina bacteriana se encuentra en la nitrogenasa.
Algunos centros 4Fe-4S participan en la acción catalítica de enzimas, pues son capaces de unirse a sustratos. Por ejemplo, el centro Fe-S de la aconitasa se une a aconitato empleando un ion de hierro carente del ligando tiolato. Este centro no experimenta una reacción redox, sino que sirve como catalizador para convertir aconitato enisocitrato. En las enzimas dependientes de SAM, el centro se une y reduce la S-adenosilmetionina para generar un radical que está involucrado en varios procesos de biosíntesis.[2]
Centro 3Fe-4S[editar]
Existen varias proteínas que contienen centros [Fe3S4], con un ion de hierro menos que la forma más común [Fe4S4]. Cada uno de los tres iones de azufre enlazan dos de hierro, mientras que el cuarto azufre enlaza a tres iones de hierro. Sus estados de oxidación pueden variar desde [Fe3S4]+ (forma todo Fe3+) a [Fe3S4]2- (forma todo Fe2+). En algunas proteínas el centro [Fe4S4] puede convertirse reversiblemente en un centro [Fe3S4] por oxidación y pérdida de un ion de hierro. Por ejemplo la forma inactiva de la aconitasa posee un centro [Fe3S4] y se activa por la adición de Fe2+ y un agente reductor.
Otros centros Fe-S[editar]
También existen sistemas polimetálicos más complejos, como los centros 8Fe y 7Fe en la nitrogenasa. La monóxido de carbono deshidrogenasa y la hidrogenasa-[FeFe] también presentan centros Fe-S inusuales.
Biosíntesis[editar]
Se conoce bien la biosíntesis de los centros Fe-S.[3][4][5] En particular, la biogénesis de los centros hierro-azufre se ha estudiado en profundidad en E. coli y A. vinelandii y en la levadura S. cerevisiae. Se han identificado al menos tres sistemas biosínteticos, denominados nif, suf e isc. El sistema nif es responsable de los centros de la enzima nitrogenasa, mientras que los sistemas suf e isc son más genéricos. En el reino animal sólo se han encontrado proteínas relacionadas con isc. El sistema isc se ha estudiado principalmente en levaduras, donde varias proteínas constituyen la maquinaria biosintética a través de la ruta de isc. El proceso se lleva a cabo con el ensamblado del centro Fe-S en una proteína de andamiaje seguido por la transferencia de un centro preformado a la proteína destino. Este primer paso sucede en el citoplasma de los procariotas o en la mitocondria de los eucariotas. En organismos superiores los centros se transportan fuera de la mitocondria y se incorporan a las enzimas extramitocondriales. Estos organismos también poseen un conjunto de proteínas involucradas en el transporte de centros Fe-S y procesos de incorporación que no son homólogos a los encontrados en organismos procariotas.
Análogos sintéticos[editar]
Los análogos sintéticos de los centros hierro-azufre encontrados en la naturaleza fueron descritos por vez primera por Richard H. Holm y colaboradores.[6] El tratamiento de sales de hierro con una mezcla de tiolatos y sulfuro permite crear derivados como el (Et4N)2Fe4S4(SCH2Ph)4].
Referencias[editar]
- ↑ S.J. Lippard, J.M. Berg (1994) «Principles of Bioinorganic Chemistry». University Science Books: Mill Valley, CA. ISBN 0-935702-73-3.
- ↑ S.C. Wang, P.A. Frey (2007). «S-adenosylmethionine as an oxidant: the radical SAM superfamily». Trends in Biochemical Sciences 32: 101-110. doi:10.1016/j.tibs.2007.01.002.
- ↑ D.C. Johnson, D.R. Dean, A.D. Smith, M.K. Johnson (2005). «Structure, function, and formation of biological iron–sulfur clusters». Annual Review of Biochemistry 74: 247-281. doi:10.1146/annurev.biochem.74.082803.133518.
- ↑ M.K. Johnson, A. D. Smith (2005) «Iron–sulfur proteins» in: Encyclopedia of Inorganic Chemistry (R.B. King, ed.), 2nd edn, John Wiley & Sons, Chichester.
- ↑ R. Lill, U. Mühlenho (2005). «Iron–sulfur-protein biogenesis in eukaryotes». Trends in Biochemical Sciences 30: 133-141. doi:10.1016/j.tibs.2005.01.006.
- ↑ T. Herskovitz, B.A. Averill, R.H. Holm, J.A. Ibers, W.D. Phillips, J.F. Weiher (1972). «Structure and properties of a synthetic analogue of bacterial iron-sulfur proteins». Proceedings of the National Academy of Sciences 69: 2437-2441. PMID 4506765. doi:10.1073/pnas.69.9.2437.
