ADN-B

El ADN-B es el modelo propuesto por Watson y Crick sobre la estructura secundaria del ADN y es la forma predominante en las células.
Estructura de la doble hélice[editar]
De 2,34 nm de diámetro, con dos cadenas antiparalelas y con los grupos azúcar-fosfato en el exterior y las bases nitrogenadas en su interior. Los pares de bases A·T y G·C se sitúan casi perpendicularmente al eje de la hélice. Dado que cada par de bases tiene el mismo tamaño, se forma una estructura regular.
Surcos[editar]

Como resultado de la asimetría de cada par de nucleótidos el ADN-B presenta surcos de tamaño diferente, y como cada par de bases gira unos 35º respecto al anterior, estos surcos se van repitiendo. Son las zonas donde las bases nitrogenadas van a ser accesibles desde el exterior. Se van alternando así dos tipos de surcos: un surco mayor y un surco menor.
La mayor capacidad informativa se encuentra en el surco mayor como consecuencia de la mayor variabilidad de los grupos químicos que presenta: en el surco mayor, los grupos químicos presentes especifican la identidad del par de base, pudiendo distinguir hasta los pares de bases A·T de los T·A, permitiendo así que las proteínas reconozcan sin equivocación las secuencias de ADN sin tener que abrir la doble hélice. El surco menor no tiene tanta abundancia de información química (no se puede distinguir entre pares de bases A·T-T·A o G·C-C·G)
Interacciones que estabilizan la estructura[editar]
El ADN-B es una estructura estable gracias a:
- Los enlaces de hidrógeno que se forman en los pares de bases: contribuyen a la estabilidad termodinámica de la doble hélice.
- El apilamiento de las bases nitrogenadas: éstas exhiben la tendencia a apilarse unas sobre otras con una orientación más o menos perpendicular al eje de la hélice, de forma que las interacciones de nubes electrónicas de los orbitales entre las bases apiladas contribuye a la estabilidad de la doble hélice.
- La hidratación de los grupos polares del esqueleto azúcar-fosfato con el entorno acuoso.
Parámetros[editar]

El sentido de la hélice es a derechas, esto es, cada una de las cadenas de nucleótidos gira a derechas: la doble hélice es una espiral dextrógira. Esto puede verificarse si nos fijamos, yendo de abajo arriba, en la dirección que siguen los segmentos de las hebras que quedan en primer plano. Si las dos hebras giran a derechas se dice que la doble hélice es dextrógira, y si giran a izquierdas, levógira.
El ADN-B tiene una estructura monótona, es decir, por cada vuelta completa o paso de rosca de la hélice hay el mismo número de pares de bases, que son 10,4. La distancia entre pares de bases es de 0,34 nm y la vuelta completa mide 3,4 nm.
La rotación por residuo (o "twist" en inglés) es el ángulo formado entre el plano de dos pares de bases consecutivos y es de un promedio de 34,6º; la inclinación por par de bases (o "tilt" en inglés) es el ángulo que formaría una línea que atravesara un par de bases respecto de la horizontal; el balanceo (o "roll") es el ángulo formado por una línea que pasara a través de dos pares de bases consecutivos; el alabeo (o "propeller twist") es el ángulo formado por el plano de una de las bases del par de bases respecto al plano de la otra (cada par de bases no siempre está en el mismo plano exacto).
Plegamiento del azúcar[editar]
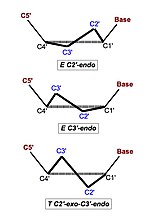
Tanto la ribosa como la desoxiribosa forman un anillo de 5 átomos que no están en el mismo plano: esto se debe a que de lo contrario las nubes de electrones se solaparían. De esta forma, uno o más átomos de carbono siempre quedan por fuera del plano en el que se encuentran los demás. Así, el azúcar puede presentar forma de sobre o forma E (del inglés envelope) cuando uno de los carbonos queda por fuera del plano, o bien forma de media silla o forma T (del inglés twist) cuando dos de los carbonos quedan por fuera del plano y en lados opuestos. Además, para cada uno de estos carbonos la conformación puede ser "endo", si el carbono está dirigido hacia donde lo está el carbono 5', o "exo", si está dirigido hacia el lado opuesto. Los únicos carbonos que pueden dar lugar a estos plegamientos son los carbonos 2' y 3'.
En el ADN-B la conformación que adopta el azúcar es E C2'-endo.
Enlaces con libertad de giro[editar]
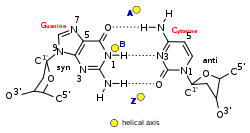
Tanto el enlace glucosídico como el enlace entre los carbonos 4' y 5' del azúcar presentan libertad de giro, lo que da lugar también a diferentes conformaciones. En el caso del enlace N-glucosídico puede aparecer la conformación "anti" si la parte más voluminosa de la base queda alejada del azúcar, o la conformación "syn" si el plano de la base nitrogenada está dirigido hacia el azúcar. La conformación "anti" es más estable que la conformación "syn".
En el caso del enlace C4'-C5' del azúcar, puede darse tres conformaciones en relación con la posición del oxígeno del C5' (O5') respecto de los enlaces C4'-O4' y C4'-C3'. Para la nomenclatura se tiene en cuenta los ángulos que se forman entre O5' y C4' y entre O5' y C3', de forma que si el ángulo es de 60° se dice que es "gauche", y "trans" si es de 180°. Como se tienen en cuenta dos ángulos, las conformaciones que pueden darse son "sinclinal +" si los ángulos son gauche-gauche, "antiperiplanar" si son gauche-trans y "sinclinal -" si son trans-gauche.
El ADN-B presenta conformación anti para el enlace N-glucosídico de todas las bases y conformación sinclinal + para el enlace C4'-C5'.
Comparación entre ADN-A, ADN-B y ADN-Z[editar]

| ADN-A | ADN-B | ADN-Z | |
|---|---|---|---|
| Sentido de giro de la hélice | Dextrógiro | Dextrógiro | Levógiro |
| Forma y tamaño | Más ancha y corta | Intermedia | Más estrecha y larga |
| Surco mayor | Estrecho, profundo | Amplio, profundidad media | Sin profundidad |
| Surco menor | Amplio, no profundo | Estrecho, profundidad media | Estrecho, profundo |
| Diámetro de la hélice | 2,55 nm | 2,37 nm | 1,84 nm |
| Unidad estructural | Par de bases | Par de bases | Dos pares de bases |
| Pares de bases/vuelta | 11 | 10,5 | 12 |
| Distancia entre pares de bases | 0,23 nm | 0,34 nm | 0,53 nm (G·C) / 0,41 nm (C·G) |
| Paso de hélice o vuelta completa | 2,53 nm | 3,54 nm | 4,56 nm |
| Rotación por residuo | 32,7º | 34,6º | –30.º |
| Inclinación de los pares de bases | 19º | 1,2º | 9º |
| Balanceo | 5,9º | -1º | –3,4º |
| Alabeo | 15,4º | 11,7º | 4,4º |
| Plegamiento del azúcar | E C3'-endo | E C2'-endo | E C2'-endo (pirimidinas) / E C3'-endo (purinas) |
| Conformación enlace N-glucosídico | Anti | Anti | Anti (pirimidinas) / Syn (purinas) |
| Conformación enlace C4'-C5' | + Sinclinal | + Sinclinal | + Sinclinal (pirimidinas) / Antiperiplanar (purinas) |
Véase también[editar]
Referencias[editar]
Bibliografía[editar]
- Watson, J. D.; Baker, T. A., Bell ; S. P.; Gann, A.; Levine, M. y Losick, R. "Biología Molecular del Gen", Médica Panamericana, 2006. ISBN 84-7903-505-6
